在科研工作中,您是否遇到过以下问题?
我想做单细胞测序,但是样品在野外采摘,只能冻存或干燥保存,难以用新鲜组织开展单细胞转录组。
听说做单细胞测序需要制备原生质体,实验室尝试很久都无法成功制备原生质体。
制备原生质体过程需要酶消化且制备时间很长,可能会触发应激反应,影响转录表达的真实结果。
我的样本部分细胞直径大于40 μm,无法被市面上大部分的仪器平台捕获。
为了有效解决植物单细胞目前研究的桎梏,单细胞核转录组测序(single-nuclei RNA sequencing,snRNA-seq)应运而生。它是指通过提取细胞核,从而在单细胞水平研究基因表达的技术。
技术原理
单细胞核转录组测序技术(snRNA-seq)不同于常规的单细胞转录组测序(scRNA-seq),不需要进行原生质体的制备,而是对组织进行切割/研磨破碎。之后利用百迈客优化细胞核分离试剂盒提取,清洗和重悬;再通过10x genomics单细胞测序平台利用微流控、油滴包裹和barcode标记等技术来实现高通量的单细胞核捕获,构建单细胞核转录组文库,借助Illumina测序平台对文库进行测序检测,即可一次性获得大量单细胞核的基因表达数据,从而实现复杂组织或珍贵冷冻样本在单细胞水平进行基因表达测序。
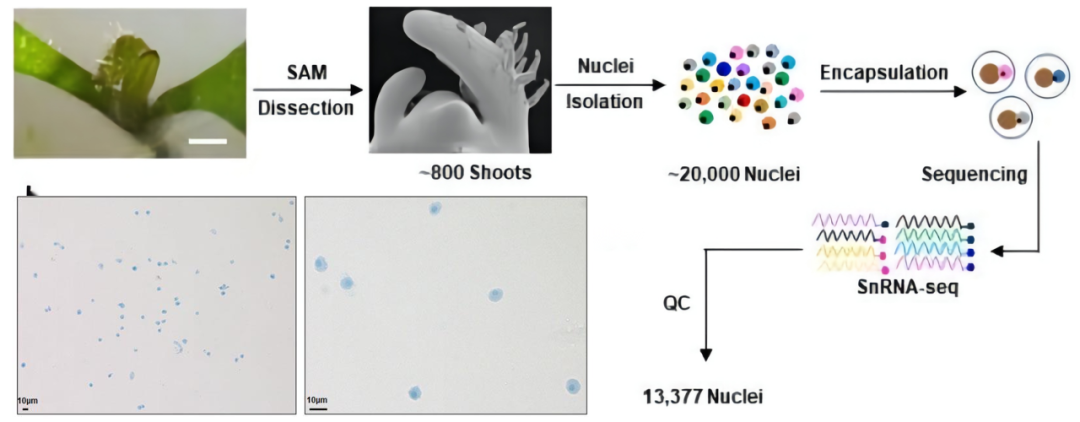
图1 番茄茎尖核提取流程及核形态展示(Tian C et al. 2020)
技术优势
1. 操作性强:无需制备原生质体,提高实验效率,缩短实验周期。
2. 更少干扰:避免原生质体制备过程诱导应激基因表达,减少“转录偏好”。
3. 轻松取材:可以实现冻存样品研究,样品保存和运输更便捷!
4. 结果可靠:基因检出率、细胞分群的结果与scRNA-seq趋于一致。
5. 兼容性强:可以开展更大尺寸的细胞研究,避免丢失重要信息。
应用案例
案例一

题目:玉米单核RNA测序揭示调控气孔运动和发育的信号网络
期刊:The Plant Cell?[IF: 12.085]?2022.2.15
发表单位:河南大学生命科学学院
样本设计:玉米叶基(n=1)、玉米果皮snRNAseq(n=3)、WT(n=4)和bzu2-1突变体(n=3)玉米叶bulk RNA-seq
主要研究结果:
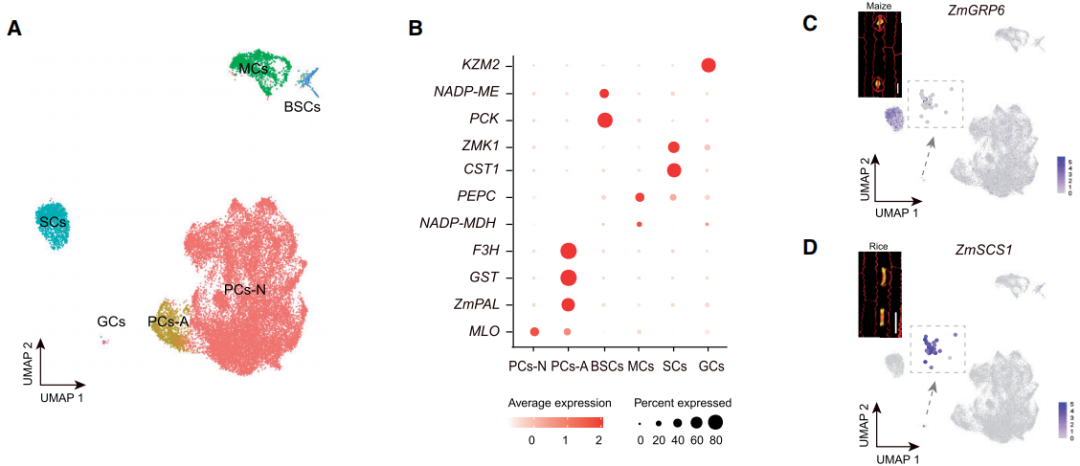
图2 玉米果皮snRNA-seq数据中的细胞类型鉴定
案例二

题目:基于单核转录组数据空间重建的拟南芥花分生组织3D基因表达图谱
期刊:Nature?Communication?[IF: 17.694]?2022.5.20
发表单位:柏林洪堡大学生物学研究所
样本设计:拟南芥花序发育的第5阶段(DEX诱导后4天)、第4阶段(DEX诱导后3天)的花分生组织snRNA-seq以及FANS分选AP3-(n=3)、AG-(n=3)样本的细胞核进行bulk RNA-seq
单细胞转录组学以分辨率表征发育器官中的基因表达异质性。然而,在这种方法中,细胞的原始物理位置丢失了。在植物中,恢复发育器官中细胞的原始位置是将基因活性与细胞特性和功能联系起来的关键。本研究从拟南芥花分生组织的7,716个细胞核中鉴定出12个主要的细胞类型。之后将单核转录组数据与基于显微复制的三维空间重建,重建了三维花分生组织中单个细胞的全基因组基因表达模式,展现了空间重建的3D单细胞转录组图谱在理解植物形态建成方面的能力。
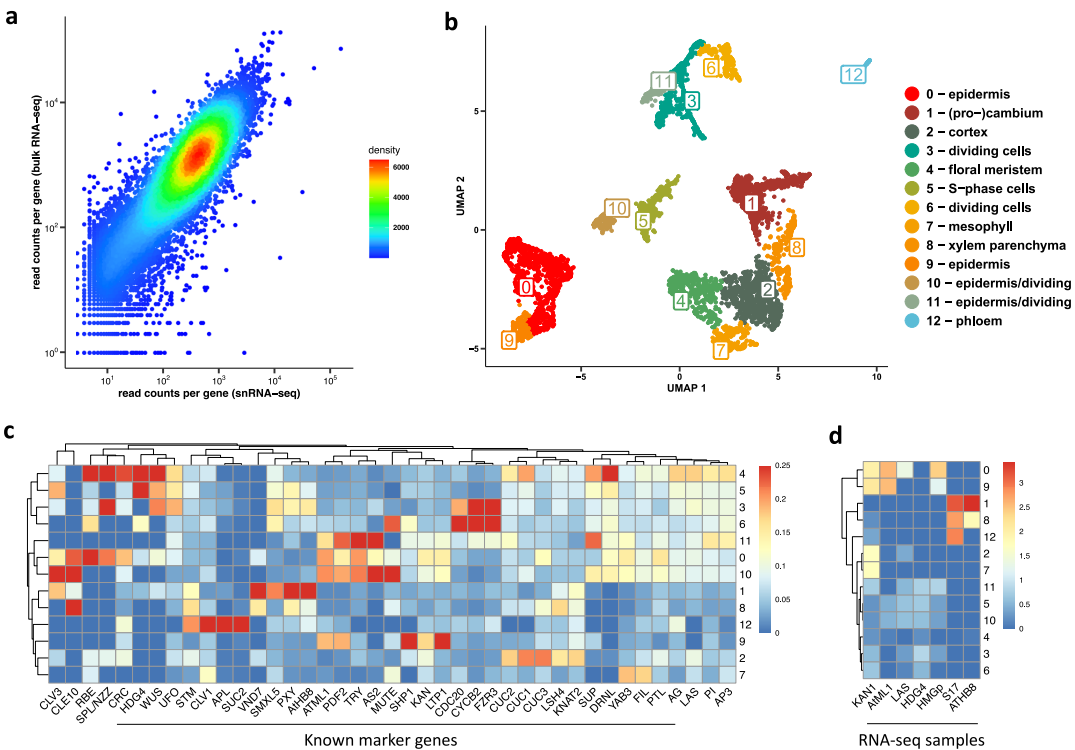
图3 拟南芥花分生组织的单核RNA测序
总 结
与单细胞转录组相比,植物单细胞核转录组在保证高效捕获分选单细胞数据的同时,减少了应激基因表达影响、胞质内代谢物的干扰。并可兼容更大细胞直径,获得更全面信息。也为特殊样本进行单细胞测序提供了新的解决方案,为进一步推动植物单细胞研究提供重要的技术支撑。
如果您对单细胞核转录组测序感兴趣,欢迎点击下方按钮联系我们,我们将为您免费设计文章思路方案。

参考文献
?
Shaw R, Tian X, Xu J. Single-Cell Transcriptome Analysis in Plants: Advances and Challenges. Mol Plant. 2021 Jan 4;14(1):115-126.
Tian C, Du Q, Xu M, et al.?Single-Nucleus RNA-seq Resolves Spatiotemporal Developmental Trajectories in the Tomato Shoot Apex.2020.?BioRxiv: 2020-2029
Sun G, Xia M, Li J, et al. The maize single-nucleus transcriptome comprehensively describes signaling networks governing movement and development of grass stomata. Plant Cell. 2022 Apr 26;34(5):1890-1911.
Neumann M, Xu X, Smaczniak C, et al. A 3D gene expression atlas of the floral meristem based on spatial reconstruction of single nucleus RNA sequencing data. Nat Commun. 2022 May 20;13(1):2838.








 京公网安备 11011302003368号
京公网安备 11011302003368号