棉花是重要的经济作物,提供了高质量的棉纤维用于工业生产和人类使用。不断增长的工业需求给棉花增产提出了更高的要求。单铃重是重要的产量构成因子之一,如何在不降低其他纤维品质的前提下提高产量是育种家孜孜以求的目标。通过MAS辅助育种能够直接对基因型进行选择。基于遗传图谱的QTL定位研究可以定位到相应的功能基因或者与功能基因紧密连锁的分子标记,因此能极大地促进MAS研究。常规的SSR标记很难构建饱和的遗传图谱,而利用SNP标记则可以解决这个问题。利用高通量测序技术能够对全基因组开发SNP标记,使高密度遗传图谱构建成为可能。
本研究利用SLAF-seq技术对包含196个子代的陆地棉RIL群体构建高密度遗传图谱,并结合多年多点单铃重的表型数据进行QTL定位。同时针对QTL定位区域进行候选基因的挖掘。
材料和方法
本文亲本是0-153和sGK9708,0-153纤维品质较好,而sGK9708产量潜力高且适应性广。双亲单铃重性状差异极显著。F6:8重组自交系196个。方法:利用SLAF-seq技术构建高密度遗传图谱并进行QTL定位。QTL定位软件:Windows QTL Cartgrapher 2.5。
结果分析
共获得443.56M reads共计87.89GB数据。数据Q20为82.24%,GC含量为34.47%。亲本共开发SLAF标签5.3万个,深度分别为78.66X和102.13X。子代平均开发5万个SLAF标签,平均深度为14.5X。基于SLAF标签共开发出160876个SNP,其中亲本中多态性有23519个,多态率为14.62%。适合棉花作图的SNP标记(aaxbb型)18318个,去除低质量、低深度和极显著偏分离的标记后后剩余5521个SNP用于遗传图谱构建。构建了棉花A基因组和D基因组连锁群26个,共3259.37cM的遗传图谱,平均图距0.78cM。其中A基因组包含标记3550个,遗传距离1838.37个,D基因组包含标记个1971个,遗传距离1971cM。
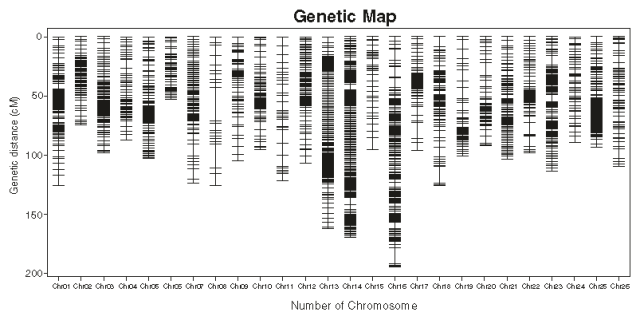
(1)遗传图与棉花物理图谱共线性分析发现图谱覆盖度良好,绝大多数的SNP与物理图谱的共线性良好,相对于A基因组而言,D基因组的共线性更好。
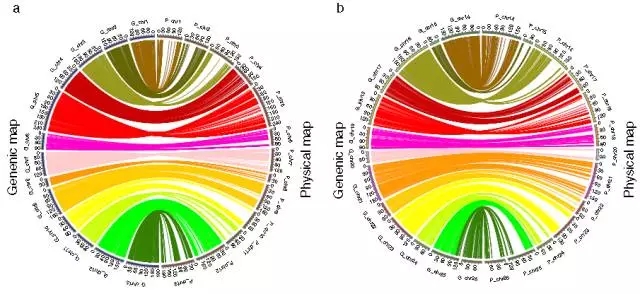
(2)重组热点分析发现26条连锁群中,21条含有重组热点区域,A套中9条LG含有重组热点,D套中12条LG含有重组热点。所有LG中,13号含有重组热点最多,有196个。
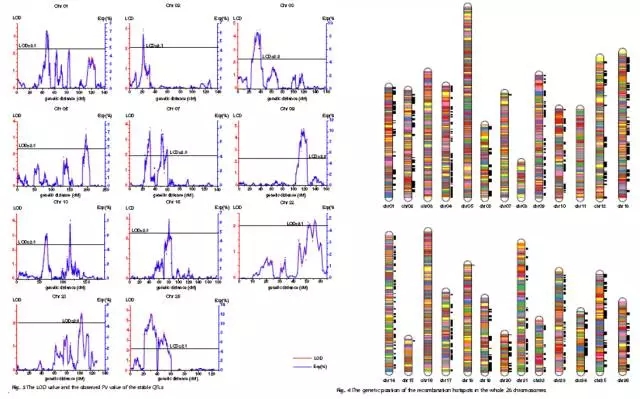
结合多年多点的表型数据进行QTL定位,共检测到11个不同环境下146个单铃重的QTL位点,其中16个能在至少3个环境中重复检测到。这16个QTLs中qBW-chr13-7能在7种环境下检测到,包含26个SNP标记,解释表型变异率在6.13%-14.7%之间。结合参考基因组共鉴定出344个候选基因,其中340个基因含有注释信息,并利用GO,KEGG和KOG数据分别进行基因富集分析。为更进一步精细定位和MAS育种奠定基础。
参考文献
Construction of a high-density genetic map by specific locus amplified fragment sequencing (SLAF-seq) and its application to Quantitative Trait Loci (QTL) analysis for boll weight in upland cotton (Gossypium hirsutum.).
BMC plant biology,2016.
]]>
好了,回到文章本身,先看看文章的材料情况:
亲本:来自鄱阳湖的母本X来自洞庭湖的父本(来自千岛湖的蚌蚌们表示不服)
子代:200个F1子代
再看文章的结果:
基本测序结果分析:
在自然状态下很难保证所有F1群体均是目标亲本的子代,所以作者进行了亲自鉴定的工作,最终剩下157个正牌的F1子代;
共获得了139,113,148个reads,其中Q值大于30以上的高质量数据占88.64%,GC含量为37.45%。父母本reads数分别为9,025,115和8,571,660,F1子代平均为773,990。与之对应的高质量SLAF-tag数为239,704个,其中父母本中开发的SLAF-tag数分别为201,805和206,806个,深度为19.25X和20.70X;子代中平均SLAF-tag为123,038个,平均深度为3.11X;
聚类分析后共获得多态性的SLAF-tag132,542个,其中可成功进行二等位编码的SLAF-tag108,004个,选择适合F1群体作图的多态性标记后,利用测序深度和完整度过滤,最终剩余4,508个多态性SLAF标记用于遗传图谱的构建;
遗传图谱构建:
结合506个SSR标记和4,508个SLAF标记,进行遗传图谱的构建,成功构建了珍珠蚌19条连锁群,共含有标记4,920个,中性图总图距为2,713cM,平均图距为1.81cM。雄性图包括3,233个标记,总图距2,561cM,雌性图包含标记3,123个,总图距2,810cM;

图1 珍珠蚌高密度遗传图谱
遗传图谱比较统计分析:
作者之前利用SSR标记做的遗传图谱和利用SLAF-seq构建的遗传图谱进行了比较。两张遗传图谱均构建了珍珠蚌19条连锁群,但是标记数,图距,分辨率均不同。SSR标记包含了506个标记,总图距1,922.3cM,平均图距3,99cM,大的Gap数较多,而基于SLAF-seq的图谱在以上指标上均显著优于SSR标记图谱。
QTL定位分析:
共定位到了26个和珍珠品质相关的QTL,分别位于第1,4,8,14,15和17号连锁群上,PVE范围为8.45%-22.8%。在1号连锁群上定位到3个壳宽QTLs,在第1和第15号连锁群上分分别定位到1个控制壳重的QTL。第8号染色体上定位到体重相关的7个QTL,另外,作者也定位到了大量其他性状的QTL。同时对第17号染色体上的4个和贝壳珍珠层颜色相关的QTL进行简单的统计验证。
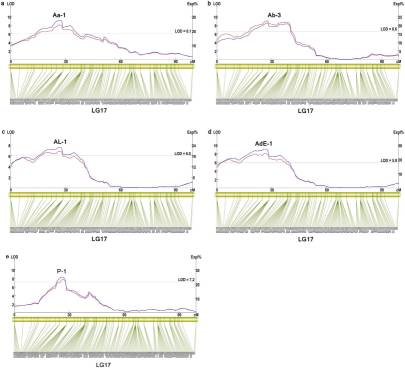
文章亮点总结:
1.材料:珍珠蚌需要生长到一定年限才能有珍珠产生,本文材料非常难得,是能获得较好结果的基础;2.有SSR遗传图谱的构建,并与SLAF标记进行了整合,图谱密度高;
3.利用遗传图谱定位到了大量和珍珠质量相关的QTL,相关标记可以进一步开发用于分子标记辅助育种,具有重要的经济价值;
4.部分QTL区域的标记进行简单的统计学验证,使QTL定位结果的可靠性增加。
本期文献解读就到这里,提前透露下,图谱君最近正在运作另外一篇水产物种的图谱构建,QTL并且利用一种高(涨)逼(姿)格(势)的方法进行QTL验证的文章,敬请期待~~~
参考文献:
Bai Z Y, Han X K, Liu X J, et al. Construction of a high-density genetic map and QTL mapping for pearl quality-related traits in Hyriopsis cumingii[J]. Scientific Reports, 2016, 6.